Открытая платформа BindCraft упрощает дизайн белков для терапии
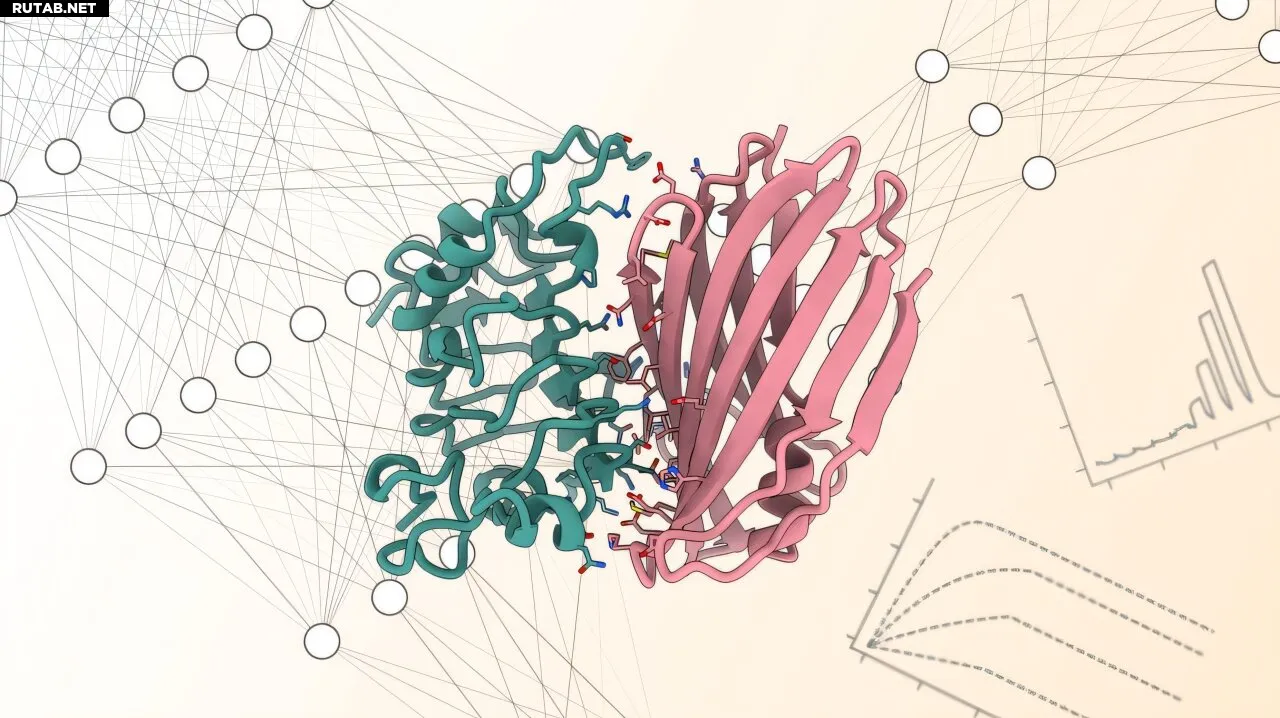
Иллюстрация белка-связывателя (розовый), взаимодействующего с целевым белком (зеленый). Автор: LPDI EPFL, CC BY SA
С момента своего выпуска в 2024 году открытая платформа BindCraft, разработанная в Федеральной политехнической школе Лозанны (EPFL), уже произвела революцию в мире дизайна белков. Физические взаимодействия между белками влияют на все: от передачи сигналов и роста клеток до иммунных реакций, поэтому способность контролировать эти взаимодействия представляет большой интерес для биологов.
Исследователи использовали нейронные сети для разработки новых белков, называемых связывателями, которые предназначены для присоединения к терапевтически значимым мишеням, подобно тому, как наша иммунная система использует антитела для связывания с патогенами. Но эти системы, использующие глубокое обучение для предсказания форм белков из последовательностей аминокислот, требуют знаний в области компьютерных наук.
«Традиционные методы обнаружения связывателей включают скрининг десятков тысяч кандидатов в белки, что требует экспериментальных возможностей и вычислительных знаний, которые не каждая лаборатория может себе позволить или имеет», — говорит Леннарт Никель, аспирант Лаборатории дизайна белков и иммуноинженерии (LPDI) под руководством Бруно Корреia в EPFL.
«BindCraft возник из желания разработать более доступный, удобный инструмент, которому нужно было бы протестировать лишь горстку белков, чтобы получить связыватель».
Вместо того чтобы вводить последовательности аминокислот в нейронную сеть и кропотливо отсеивать полученные связыватели для хорошего совпадения, команда EPFL в сотрудничестве с учеными из MIT использовала структуры, загруженные в систему AlphaFold2 от Google DeepMind, для генерации последовательностей новых связывателей на основе набора желаемых функциональных свойств — таких как связывание с конкретной мишенью.
Обратный инжиниринг
«С BindCraft мы, по сути, проводим обратный инжиниринг текущего конвейера, используя сеть предсказания структуры белка с самого начала для генерации новых связывателей, обладающих свойствами, которые мы ищем», — объясняет аспирант Кристиан Шелльхаас.
Сосредоточившись на небольшом количестве дизайнов связывателей, а не на высокопроизводительном скрининге огромных библиотек кандидатов, BindCraft делает дизайн белков более эффективным, а также более демократизированным.
Команда опубликовала свои результаты в журнале Nature в сотрудничестве с исследователями из Швейцарии, США и Нидерландов.
Качество вместо количества
В своем исследовании команда проверила связыватели, разработанные для взаимодействия с дюжиной биотехнологических и терапевтических молекул, включая AAV (адено-ассоциированные вирусы), которые используются для доставки терапевтических генов в целевые клетки; нуклеазу CRISPR-Cas9, используемую в приложениях для редактирования генов; и некоторые распространенные аллергены.
Эксперименты показали, что связыватели команды присоединялись к своим целевым мишеням со средним показателем успеха 46%, что открывает возможность большего терапевтического контроля.
«Для AAV идея заключается в использовании этих новых связывателей для обеспечения доставки генов только в определенные клетки и ткани, минимизируя риск потенциальных побочных эффектов. В случае CRISPR-Cas9 наши связыватели могут остановить его активность по редактированию генов и предотвратить его действие тогда и там, где не следует», — объясняет первый автор и ученый LPDI Мартин Пачеса.
С момента первоначальной публикации BindCraft в виде препринта платформа уже быстро и с энтузиазмом была принята биологическим сообществом, вызвав запросы от пользователей на модификации и дополнительные функциональные возможности.
«Мы были удивлены тем, как быстро наш инструмент был принят — он даже уже используется в промышленности. Запросы от пользователей — это большое вдохновение для продолжения разработки нашего метода. Мы уже работаем над адаптацией BindCraft для меньших терапевтически значимых молекул, таких как пептиды», — говорит Пачеса.
Больше информации: Martin Pacesa et al, One-shot design of functional protein binders with BindCraft, Nature (2025). DOI: 10.1038/s41586-025-09429-6
Источник: Ecole Polytechnique Federale de Lausanne







0 комментариев