Ученые представили новые инструменты для изучения микромира
Исследователи из Университета штата Аризона представили два новых инструмента, которые упрощают и делают более точным анализ микроорганизмов. Эти разработки помогут в изучении микробиомов, отслеживании болезней и экологическом мониторинге.
Цифровое дерево, построенное на основе ДНК-подобных связей, иллюстрирует, как ученые отслеживают происхождение микробов. Новые инструменты, такие как TMarSel и scikit-bio, помогают строить более четкие семейные деревья микроорганизмов. Графика: Biodesign Institute.
Первый инструмент, TMarSel (Tree-based Marker Selection), автоматически выбирает оптимальные генетические маркеры для построения эволюционных деревьев микробов. Это особенно важно для метагеномики, где ученые работают с миллионами геномов из окружающей среды, часто неполных.
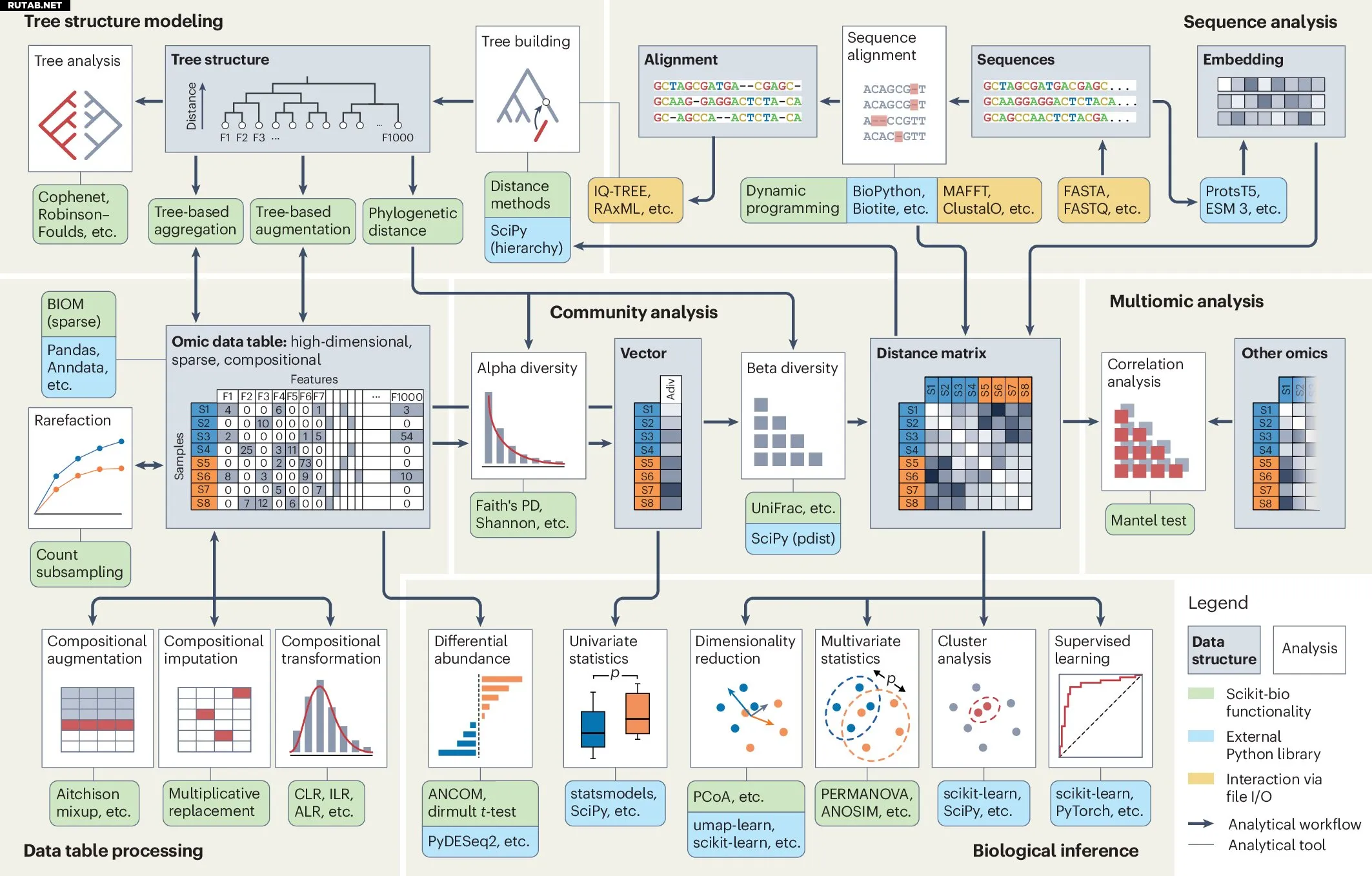
Второй инструмент — это открытая программная библиотека scikit-bio для языка Python. Она предоставляет более 500 функций для анализа больших биологических данных, сравнения микробных сообществ, работы с последовательностями ДНК и подготовки данных для машинного обучения.
Возможности scikit-bio для анализа биологических данных и его взаимодействие с другими инструментами экосистемы Python. Автор: Nature Methods (2025).
«Мы создаем инструменты с открытым исходным кодом, потому что верим, что когда каждый может получить к ним доступ и развивать их, выигрывает всё научное сообщество», — сказал ведущий исследователь Циюнь Чжу.
Оба исследования были опубликованы в журналах Nature Communications и Nature Methods. Библиотека scikit-bio уже процитирована в десятках тысяч научных работ.
ИИ: Эти инструменты выглядят как важный шаг к стандартизации и автоматизации анализа микробиологических данных, что критически важно в эпоху, когда объем генетической информации растет экспоненциально. Их открытый характер может значительно ускорить исследования в медицине и экологии.




0 комментариев